2018年5月29日,国际著名期刊《Nature communications》在线发表了中国科学院生物物理研究所周政课题组与美国克利夫兰Lerner Research Institute 的Zihua Gong课题组合作完成的研究论文“Structural basis for recognition of 53BP1 tandem Tudor domain by TIRR”。 该项研究首次详尽揭露TIRR抑制53BP1识别组蛋白修饰H4K20me2的分子机制,对进一步了解细胞的DSB修复通路具有重要意义。
真核细胞中对于DSB(DNA Double Strand Break)有两种主要的修复方式:非同源末端连接(NHEJ,non-homologous end-joining),以及同源重组(HR,homologous recombination)。两种不同的DSB修复途径各在不同的细胞周期中发挥作用,从而确保基因组遗传物质的稳定。53BP1蛋白是NHEJ途径中的重要上游调控因子,它通过其串联Tudor结构域识别损伤染色质上H4K20me2修饰,从而被招募至染色质上发挥其招募下游效应因子的重要功能,进而影响整个NHEJ修复途径。而TIRR是新鉴定出来的目前唯一一个天然的组蛋白甲基化reader抑制蛋白,它能够和53BP1的串联Tudor结构域直接相互作用,阻断其Tudor结构域对H4K20me2的识别,从而抑制53BP1 被招募至染色质上发挥下游功能。这也是细胞针对DSB修复通路的一种重要调控方式。但由于结构信息的缺乏,TIRR是如何调控53BP1并抑制其被招募至染色质上的,这一过程并不清楚。
在这项研究中,研究人员解析了TIRR/53BP1 Tudor复合物的1.76-埃分辨率晶体结构。结构显示TIRR通过其N端区域以及关键的L8 loop结合并占据53BP1的Tudor结构域,诱导Tudor结构域上用于阅读H4K20me2分子标记的芳香笼结构发生了明显的构象改变,从而失去了对H4K20me2的识别能力。此外,通过生物化学、生物物理学、细胞生物学等多种方法说明结构中发现的关键氨基酸在TIRR/53BP1相互作用中具有重要影响。通过对TIRR的氨基酸序列进行分析,我们还发现位于L8 loop上的His106是TIRR在进化过程中获得的一个独特的氨基酸,并且其对于TIRR调控53BP1十分重要。最后,通过结构指导的定点突变方法还筛选出了相对于野生型TIRR对53BP1具有更强结合能力的TIRR突变体,对Tudor结构域等组蛋白甲基化reader蛋白的小分子药物设计具有重要的指导意义。
该项工作由中国科学院生物物理研究所周政课题组与美国克利夫兰Lerner Research Institute 的Zihua Gong课题组合作完成。中科院生物物理所周政研究员和Lerner Research Institute的Zihua Gong研究员为本文的共同通讯作者。周政课题组博士研究生戴亚鑫、Zihua Gong课题组助理研究员Aili Zhang、周政课题组副研究员单珊为文章的共同第一作者。该研究获得国家自然科学基金、科技部973计划、中国科学院战略性先导科技专项(B类)等资助。生物物理所表观遗传团队的其余成员在研究过程中提供了重要帮助。
文章链接:https://www.nature.com/articles/s41467-018-04557-2
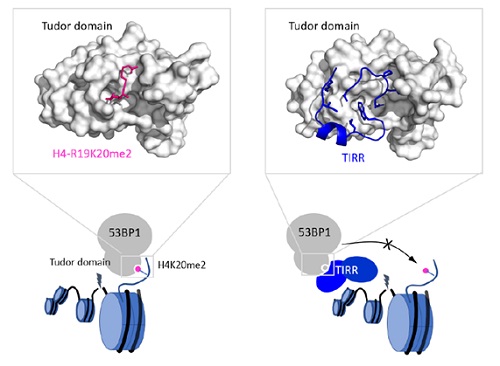
图示:TIRR抑制53BP1 Tudor对H4K20me2识别的分子机制。
供稿:周政课题组